+49 (0) 3727 / 58-1242

LaNa-Sax
Lasergestützte Strukturaufklärung in FRET gestützten RNA de novo Modellen
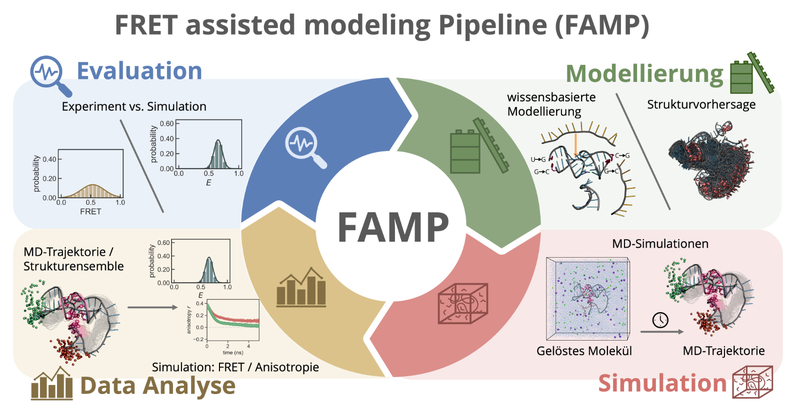
Das zentrale Ergebnis dieses Teilprojekts ist ein Software-Framework, das die integrative Modellierung nicht-kodierender RNA auf Basis von Förster-ResonanzFRET-Daten vereinfacht und automatisiert. Eine Python-basierte Pipeline bündelt den gesamten Workflow von der Strukturvorhersage bis zur Simulation experimenteller Daten in einer einheitlichen Umgebung. Durch die modulare Struktur mit den Klassen Modeling, MDSimulation und DataAnalysis lassen sich komplexe Arbeitsschritte wie die Bestimmung photophysikalischer Parameter effizient per Funktionsaufruf ausführen.
Ein besonderer Fortschritt ist die neu entwickelte FRET-gestützte Selektion von RNA-Strukturen. Sie ermöglicht es, große Mengen in silico erzeugter Strukturmodelle automatisiert zu filtern und gezielt jene auszuwählen, die experimentelle FRET-Verteilungen am besten abbilden. Hier geht es zur Veröffentlichung: https://doi.org/10.1093/nar/gkag147
Die Pipeline ist in Docker verfügbar, plattformunabhängig nutzbar und über Jupyter-Notebooks bedienbar. Als Open-Source-Software auf GitHub steht das Framework der wissenschaftlichen Community dauerhaft zur Verfügung: https://github.com/BoernerLab/FAMP_rna
Das Projekt wird dankenswerter Weise aus Mitteln des Freistaates Sachsen und der Europäischen Union im Rahmen einer ESF-Plus-Nachwuchsforschergruppe im Zeitraum vom 01.01.2023 - 31.12.2025 gefördert.